- Productos
- Módulo de software de análisis
- JSI medical systems
Módulo de software para secuenciación SEQPATIENTde análisisde laboratorio
Añadir a mis favoritos
Añadir al comparador
Características
- Función
- de análisis
- Aplicaciones
- para secuenciación, de laboratorio
Descripción
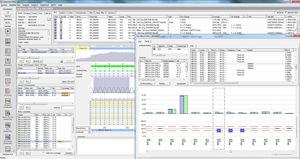
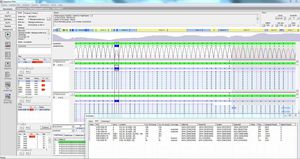
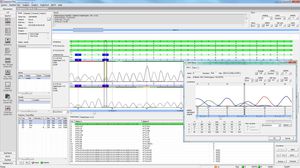
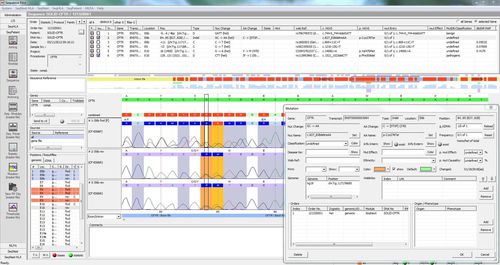
SEQPATIENT es una aplicación potente y fácil de usar para la alineación y detección de variantes de datos de secuenciación Sanger. SEQPATIENT puede analizar datos de todas las plataformas de secuenciación comunes. La visualización de todas las variantes detectadas como deleciones, inserciones, indels y SNPs es clara e intuitiva. Es posible el análisis de ADN genómico y ADNc. Una función estadística de área de pico garantiza la detección de mutaciones de baja frecuencia como abandonos alélicos, mosaicos y variantes somáticas.
SEQPATIENT ofrece acceso a bases de datos SNP públicas como dbSNP, 1000 Genomes, COSMIC, ClinVar, ClinVitae, ExAC y gnomAD para clasificación y filtrado. Todos los datos de los resultados pueden intercambiarse con nuestra base de datos de variantes para la Experiencia y el Conocimiento Compartidos - varSEAK, transferirse a los Sistemas LIM internos del laboratorio y/o emitirse como informes personalizados de pacientes.
Compatible con datos de todas las plataformas comunes de secuenciación Sanger
Fácil configuración de regiones objetivo individuales mediante la importación de archivos txt o bed basados en genes individuales descargados (ENSEMBL / NCBI) o hg19 / hg38
Llamador de bases configurable con umbrales dependientes del secuenciador
Recorte automático y definido por el usuario de los archivos de resultados de secuenciación
Identificación de pacientes y genotipado mediante SNP IDs
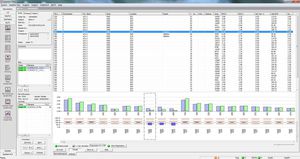
Todos los resultados de un paciente se muestran en una pantalla, incluidas las variantes encontradas, los cambios de aminoácidos, las nomenclaturas HGVS, etc.
Alta sensibilidad y especificidad para la detección de SNP, deleciones, inserciones e indels
Base de datos interna de mutaciones que mantiene un registro del historial de detección de mutaciones de SEQPATIENT y SEQNEXT
---
Catálogos
SEQUENCE PILOT
2 Páginas
Otros productos de JSI medical systems
Products
* Los precios no incluyen impuestos, gastos de entrega ni derechos de exportación. Tampoco incluyen gastos de instalación o de puesta en marcha. Los precios se dan a título indicativo y pueden cambiar en función del país, del coste de las materias primas y de los tipos de cambio.